水の風土記
たったバケツ一杯の水から、そこに棲む魚が明らかに!

目の前に広がる海や湖沼を眺めて「ここにはどんな魚が棲んでいるのだろう」と思ったことはありませんか? 生息する魚類を調べるには網で捕えたり釣りあげたり、あるいは潜って目で確認するなど大変な時間と労力がかかりました。ところが、「水を汲むことで、そこに棲む魚類がわかる」という画期的な方法が生まれたのです。それを編み出したのは、遺伝子の本体であるDNAを用いて3万種を超える魚類の進化の歴史を解き明かしてきた宮正樹さん。ウナギやマグロは深海に起源があることも突き止めた世界的に有名な研究者である宮さんが、魚の糞(ふん)などとともに放出されて水のなかを漂う魚類の「環境DNA」を利用したのです。どうしてそのようなことができるのか、またどのような可能性があるのかをお聞きしました。
-

-
千葉県立中央博物館 生態・環境研究部 部長
宮 正樹 (みや まさき)さん - 1959年(昭和34)東京都生まれ。東京大学大学院農学研究科博士課程修了。農学博士。学位取得後に千葉県立中央博物館へ就職。専門分野は魚類を中心とした分子生態学・分子進化系統学。研究テーマは遺伝子の情報を利用して魚の生態や進化的起源を探ること。発表した論文は140にのぼり、国内外の専門書や論文に9500回以上引用されている。著書に『新たな魚類大系統――遺伝子で解き明かす魚類3万種の由来と現在』(慶應義塾大学出版会 2016)がある。趣味は料理、ワイン、ガーデニング。年に1〜2回は渡仏し、ワインの産地を巡っている。
今いる魚類3万数千種も、もともとは1つの共通祖先
ヒトの子どもが親に似た顔をしているのは、父母から受け継いだ遺伝子が発現しているからです。こうした遺伝子のつながりは、どこまでも伸びる長い糸のように何世代にもわたってずっと続いています。これを気の遠くなるほどたぐり寄せ、600万年ほど遡ると、ヒトともっとも近縁な類人猿であるチンパンジーとヒトが分岐したとされる、たった1種の共通祖先にたどりつくのです。
この600万年前に存在したであろう仮想的な(それがどんな動物かはわかりません)共通祖先からヒトとチンパンジー両種の祖先が生まれて、それぞれ別の道をたどって進化しました。したがって、よく一般的に「ヒトはサルから進化した」といわれますが、その言い方は誤りで、より正しくは「ヒトとサル(チンパンジー)は共通の祖先をもつ」といわなければなりません。
このように遺伝子を分析して遠い過去に遡り、生物間の系統関係を明らかにする研究に私は携わってきました。その対象は魚類です。現生の魚類約3万数千種も、大昔に生まれたたった1種の祖先から、5億年もの歳月をかけて種分化や絶滅を繰り返しながら現在に至ったものです。したがって遠近の差はあるものの、現生魚類3万数千種の間には、親子関係を最小単位とした血縁関係が存在します。
親子間で受け渡される遺伝子の本体はDNAという物質です。DNAには異なる塩基をもつ4種類(A・G・C・T)があり、それらが2本の相補的な鎖状に連なった塩基配列として遺伝情報を蓄積しています。DNAの塩基配列にはランダムな突然変異が生じ、その総量は時間とともに増加します。塩基配列の違いを種間で比較・解析すれば、現生生物の血縁関係(系統関係)を推定できるのです。従来は見た目の形態や解剖学的特徴のみに着目して分類されていた魚類の大系統が、こうした研究成果によって次第に書き換えられています。
私たちの研究グループは、魚類の大系統の解明をめざし、細胞内小器官であるミトコンドリアのゲノム(全遺伝子情報)の全長配列を簡単に素早く解析する方法を開発しました。これを魚種ごとに比較すれば系統関係がたどれるわけです。その結果として、マグロやウナギの祖先が深海魚だったことがわかったり、また似ても似つかない姿をしているけれどウナギの仲間の祖先に近い形態をもつとされる、生きた化石「ムカシウナギ」の発見につながるなど、マスメディアに取り上げられるような話題も提供することができました。
研究費を失ったどん底から「環境DNA」に挑む
私は、何をするにしても自分なりに方法を工夫することが習慣のようにしみついています。父が「ビニールハウス加温器」や「泡で流すトイレ」などを初めてつくった発明家でしたので、その影響があるのかもしれません。趣味の釣りやガーデニングもそうですし、もちろん本職の研究もです。
そういう性分なので、世界最先端の研究に追随するとか他人が立てた仮説を検証するといった仕事には面白味を感じません。誰も見つけなかったことを発見するのが何よりも好きで、そこにこそ生きがいを感じます。
先ほどお話しした「遺伝子を分析して魚類の大系統を解明する研究」は、最初のうちはとてもエキサイティングで、ものすごい勢いでおもしろい事実が次々と見つかりました。しかし、やはり十数年も経つと、どうしても過去の延長になり、自分の研究を確証していくだけの面白味のない道筋しか見えなくなります。それに、この分野においしいネタがたくさんあるとわかれば、一挙に予算と人員を投入して勝負をかけてくるアメリカなどにはかなうはずもありません。だんだん気力も続かなくなりました。
そんな折りの2014年4月、自分では「いける」と思って申請した日本学術振興会の科学研究費(科研費)助成が不採択になり、大いに慌てました。このままでは予算ゼロで丸一年つぶれてしまうし、翌年申請しても採択されるどうかわかりません。何か他に手立てはないか必死に探したところ、科学技術振興機構(JST)の「戦略的創造研究推進事業」で「海洋生物多様性および生態系の保全・再生に資する基盤技術の創出」というプロジェクトを募集しているのを見つけました。
そこでふと思い出したのが、2年前に送られてきたデンマークの研究者の「環境DNA」に関する論文です。その論文の主旨は「海水を汲み取り濾過して集めたDNAを分析すれば、そこに棲む魚を検出できる」というもの。当時はなんだか怪しい、いんちきくさいと信用していなかったし、研究者仲間も同意見でした。
ところが、改めて論文を読み直してみると、私のもつ魚類に関するDNAの経験と知識を駆使すれば、もっとよいツールができるし、DNA検出のしくみそのものを高度化できる、という確信を得たのです。そこで、日本でいち早く環境DNAに注目して研究していたグループに連絡を取り、一緒に研究しませんかと私の方法を提案しました。それが受け入れられて、先のプロジェクトに共同で申請したところ、幸い採択されました。私にとってはまったく新しい研究分野となりますが、2014年10月から5年半のプロジェクトがスタートしたのです。
海中のDNAを調べればどんな魚がいるかわかる
環境DNAとは、例えば魚類や両生類など大型生物の体内から放出されたDNAのことを指します。水中にいる単細胞のバクテリアや植物プランクトンではありません。しかし、その由来はまだ特定されていません。魚類なら糞と一緒に腸壁を通って剥がれ落ちた細胞かもしれないし、エラ呼吸を通じて排出された細胞かもしれない。いずれにせよ、環境DNAを使えばどんな種類の魚がどこにいるかわかるのです。水中がもっとも調べやすいのですが、土中や空中などでも分析できます。
DNA解析にはポリメラーゼ連鎖反応(PCR)という増幅手法を使います。私たちの身体のなかでもDNAはどんどん複製されています。そうでないと細胞は死んでしまいますから。その複製を人工的に2倍、4倍、8倍、16倍……と30回くらい繰り返すと、もともと微量だったDNAを分析可能な量に増幅できます。これがPCRという手法です。この原理を考案した人はノーベル賞を受賞しました。
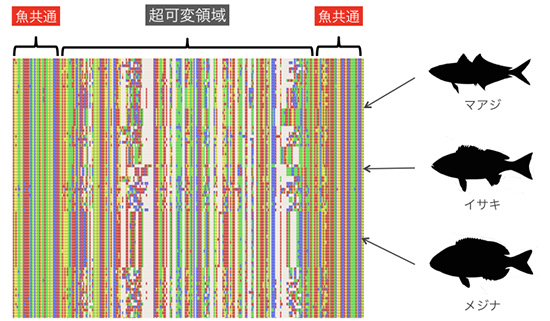
私がミトコンドリアゲノムの全長配列を読む研究を通じて開発したのが、PCRに使うツールの一つです。どの魚も共通してもっている2カ所に挟まれた、変化の激しい短い領域を増幅するツールを開発し、「MiFish(マイフィッシュ)プライマー」と名付けました。Miはミトコンドリアの略語と私の名字の頭文字です。このMiFishプライマーを使ってPCRによりDNAの断片を増幅し、次世代シークエンサーという機器で高速に塩基配列を決定します。このような、環境DNAを用いたメタバーコーディング(同時並列多種検出系)法を使えば、水中にどんな魚がいるか正確に素早く判定できるはずと考えたのです。
まずは魚種がわかっている水族館で検証しました。沖縄美ら海水族館の4つの大型水槽の水を汲んで濾過して、フィルターに残ったDNAを解析すると93%以上の魚種を検出できたのです。正直、これほどうまくいくとは思っていませんでした。一連の実験結果を報告した論文を英国王立協会のウェブ科学ジャーナルに発表したところ、国内で大きな反響を呼び、「バケツ一杯の水で海や川に棲んでいる魚を判定する技術」として多くのメディアでも紹介されました。
その後の研究で、天然海水でも良好な結果が得られることがわかっています。ベーリング海、厚岸湾、久米島の珊瑚礁や深層水などで「まるで水のなかを見てきたようなデータ」が得られているのです。例えば、14日間の潜水調査で目視された魚が80種だった舞鶴湾では、たった1日の環境DNA調査で128種の魚が検出されました。今は房総半島沿岸11の測定箇所で調査していますが、1カ所で60〜80種の魚を検出できます。時期をずらして定点観測すれば、常に同じ魚がいるわけではない海のなかのダイナミックな変化をデータで示せるのです。
サンプルの採取方法は、まず岸からバケツを投げて海水を汲み、シリンジ(注射器)で吸い上げ、ステリベクスと呼ばれるフィルターが入ったカートリッジを取り付け加圧濾過します。バケツの海水から2回、計100ミリリットルを濾過。その総量が1リットルに達するまで、この作業を計10回繰り返すのです。ステリベクスにDNAの劣化を防ぐ薬品を充填し、実験室に持ち帰りDNAを抽出・解析します。空中には他の生物のDNAが漂っているので、コンタミ(contamination=汚染)を防ぐため実験室は清潔にしなくてはなりません。
環境アセスメントから「今週のサンマ予報」まで
今のところ私たちの研究グループは、採取した環境DNAによって魚種を特定するためのデータとして、MiFishプライマーで増幅される領域(リファレンス配列)を7,000種ほど揃えています。これは日本沿岸産の魚種だと六十数%に相当します。世界中で研究が進んでいるので、現生魚類約3万数千種のデータがそろうのは時間の問題です。そうなれば、環境DNA調査で水中に棲息する魚の正体がほぼすべてわかることになります。
今夏(2017年)、日本の海岸約550カ所で30チームが手分けし、南は与那国島から北は礼文島まで「全国一斉魚類相調査」を実施しました。千葉県木更津市にあるかずさDNA研究所で採取したDNA を解析しているところです。この夏、日本沿岸のどこにどんな魚がいたか、見てきたようにわかるはずです。こうしたモニタリングを続ければ、海洋資源を適切に管理するためのデータを提供できるでしょう。
環境DNAによるメタバーコーディング法が画期的なのは、基本的な分子生物学の実験技能と基本的なコンピュータの知識さえあれば「だれでも、いつでも、どこでも」使える技術であることです。これまでは、水中にいる魚を知るには採集するか潜水して目視で観察するしかありませんでした。それでも棲息する魚種を完全に把握できず、しかも魚に関する専門知識がなければ種の同定もできません。こうした課題を一挙に解決する、世界中で使用可能な技術なのです。
対象は魚類に限りません。ボルネオの熱帯雨林には塩の析出する泉「塩場」があります。森の動物がミネラル源を求めて水を飲みに来るのですが、ここでオランウータンやゾウなどの絶滅危惧種を調べるために、哺乳動物用に改良した「MiMammal(マイマンマル)プライマー」を使いました。水のなかと同様に森のなかもこれまでブラックボックスでした。そこに棲む動物を把握するにはカメラを仕掛けてその姿を撮影するという、いわば偶然に頼るしかなかったのですが、この技術を使えば一発でわかるのです。鳥類用には「MiBird(マイバード)プライマー」をつくっています。水を浴びに来る鳥、水を飲みに来る鳥も把握できるのです。
この技術の用途は、生物多様性調査、環境アセスメント(影響評価)から資源管理、食糧問題まで、まさに限りがありません。さらに進歩すれば、魚の群れがどこに動くか、多くの地点で連続的にモニタリングできるようになるはずです。その結果としてビッグデータが蓄積されれば、「明日のマグロ予報」や「週間サンマ予報」のような「魚の天気予報」さえ実現可能かもしれません。
発見することが大好きな私としては、「未知種の発見」につながるはずなのでとてもワクワクします。沖縄の久米島は、深層水を汲み上げる海洋温度差発電の実証設備ができたおかげで、海洋深層水を利用したクルマエビ養殖の一大産地になりました。深海の水は清潔なので病気にかかりにくいため、ウミブドウやカキもその水で養殖しています。海洋深層水には他にも化粧品や飲料水などさまざまな用途がありますが、その久米島で私は80種類ほどの深海魚を検出しました。何回か調査を続ければ、きっと未知の魚も検出されるでしょう。
(取材日 2017年10月23日)